#########1.データの取り込み,整形#########
#install.packages("kernlab") ※初回のみ実行
library(kernlab)
data(spam)
attributes(spam)$names #項目名を確認
#項目名の解説は、http://archive.ics.uci.edu/ml/datasets/Spambaseに掲載されている
#データ型を確認
for (i in 1:ncol(spam)) {
print(c(names(spam[i]),class(spam[,i])))
}
#欠損値の有無
sum(is.na(spam))
#ヒストグラムで分布を確認
par(mfrow=c(8,8),mar=c(0,0,0,0),ps=10) #レイアウト調整
for (i in 1:(ncol(spam)-1)) {
hist(spam[,i],main=names(spam[i]))
}
#対数をとるべき形状をしているが、0値が多数を占めるため回避
#相関行列確認
spam_cor <- cor(spam[,1:57])
#install.packages("corrplot") #初回のみ実行
library(corrplot)
par(mar=c(6,3,3,3),mfrow=c(1,1),ps=10) #余白幅の調整。順に底辺,左,上,右の順。
corrplot(spam_cor) #中央(labs~direct)あたりに相関が強い変数が集積している
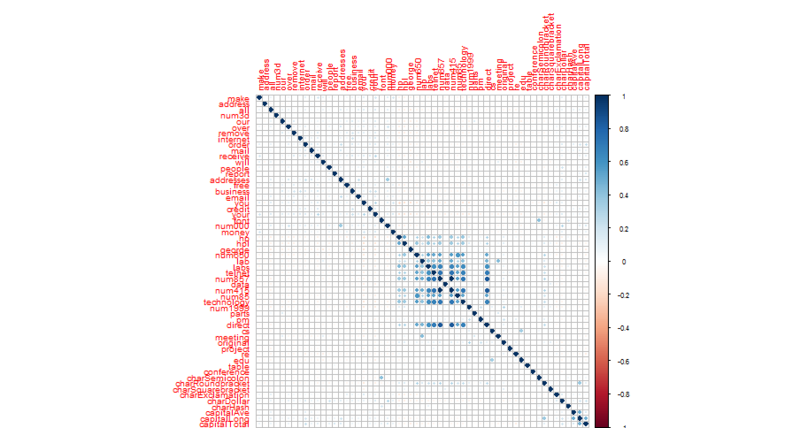
#相関が一定値を超えるような変数を抽出する関数を定義
cor.check <- function(X,q) {
val <- NULL
COR <- cor(X) #X needs to be numeric data
k = 1
for (i in 1:nrow(COR)) {
for (j in 1:ncol(COR)) {
if (COR[i,j] >= q && i > j) {
#オブジェクトを格納する場合に[[]]を使用する
val[[k]] <- c(c(names(X[i]),names(X[j])),c(i,j),COR[i,j])
k = k + 1
}
}
}
val
}
cor.result <- cor.check(spam[,1:57],0.9)
#相関が0.9を超える変数の組を抽出
#0.9の目安については「マーケティングのための多変量解析」p.106による
cor.result
#相関が0.9を超える変数のうち片方をそれぞれ削除
delete <- rep(0,length(cor.result))
for (i in 1:length(cor.result)) {
delete[i] <- cor.result[[i]][3]
}
delete <- unique(as.numeric(delete))
spam_rv <- spam[,-delete]
#厳密には目的変数との相関関係が低い方の説明変数を削除すべきだが、今回は割愛
#標準化
spam_rv[,1:(length(spam_rv)-1)] <- scale(spam_rv[,1:(length(spam_rv)-1)])
spam_s <- spam_rv
#########2.Validate data, Train dataの生成#########
set.seed(2) #一定の結果を得るための乱数セット
trainNO <- sample(nrow(spam_s),nrow(spam_s)*0.8,replace=FALSE) #replace=TRUE:非復元一様分布からの抽出
train_dat <- spam_s[trainNO,]
vali_dat <- spam_s[-trainNO,]
#まずはそのまま実行
names(train_dat)
#family=binomialは目的変数が0,1の場合に使用
train.glm <- glm(type~.,data=train_dat,family=binomial)
summary(train.glm)
#AICに基づいた変数選択法(デフォルトはbackward)
train.glm1 <- step(train.glm)
summary(train.glm1)
#########3.モデルの評価#########
#(a)残差分析
par(mar=c(4,4,4,4),mfrow=c(2,2),ps=20)
plot(train.glm1)
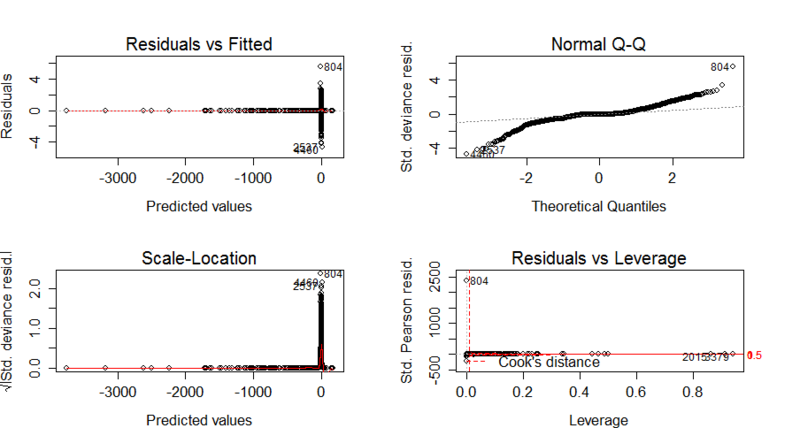
#外れ値である804,4460,2537,2015,3379を除いて再度ロジスティック回帰分析
delete2 <- c(804,4460,2537,2015,3379)
spam_rv2 <- spam_s[-delete2,]
trainNO2 <- sample(nrow(spam_rv2),nrow(spam_rv2)*0.8,replace=FALSE) #replace=TRUE:非復元一様分布からの抽出
train_dat2 <- spam_rv2[trainNO2,]
vali_dat2 <- spam_rv2[-trainNO2,]
train.glm2 <- step(glm(type~.,data=train_dat2,family=binomial))
par(mar=c(4,4,4,4),mfrow=c(2,2),ps=20)
plot(train.glm2)
summary(train.glm2)
library(DAAG)
vif(train.glm2) #多重共線性の問題はなし
#外れ値が残るが無視(何度繰り返しても解決しないため)。
#Predicted Values=0付近 ⇔ log(p/1-p)=0付近⇔p=1/2付近
#にて予測誤差が大きいことに注意する。
#(目的変数の実績値はspam/nonspamの値しかとらないので当然のことと想定)
#(b)オッズの評価
par(mfrow=c(1,1),ps=15)
summary(train.glm2)$coefficients
#どの要素がより影響しているか確認。オッズを説明変数毎に算出
exp(sort(train.glm2$coefficients,decreasing=TRUE))
plot(sort(exp(train.glm2$coefficients),decreasing=TRUE))
#オッズの95%信頼区間 ※とりあえずオッズ10位10変数。z値, 標準偏差も付記
select <- c("num3d","capitalLong","capitalAve","charDollar","remove","charHash","free","num000","credit","num650")
oddslist <-cbind(exp(confint(train.glm2))[select,1],
exp(summary(train.glm2)$coefficients[select,1]),
exp(confint(train.glm2))[select,2],
exp(summary(train.glm2)$coefficients[select,2]),
summary(train.glm2)$coefficients[select,3:4])
colnames(oddslist) <- c("2.5%","exp(coef)","97.5%","exp(std.Er)","z val","pr(>|z|)")
oddslist
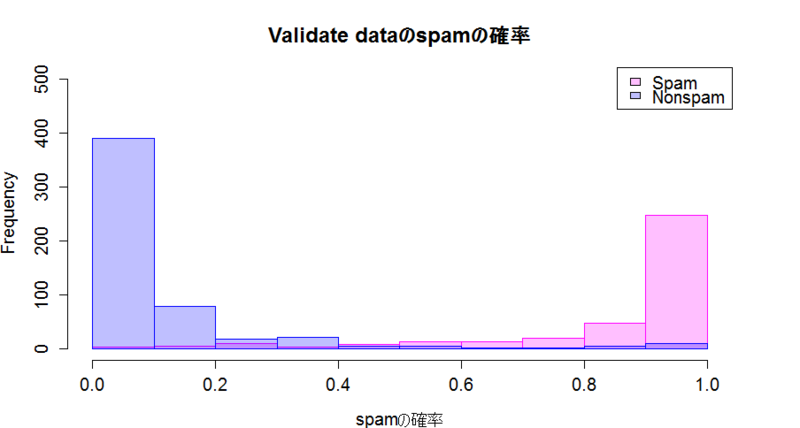
#(c)予測のヒストグラム
#まず、vali_datをSurvivedがYes/Noのグループに分割
vali_datNo <- subset(vali_dat2, type=="nonspam")
vali_datYes <- subset(vali_dat2, type=="spam")
#それぞれにモデルを適用し、spamである確率を予測
vali_datNo$P <- predict(train.glm2,newdata=vali_datNo,type="response") #type="prob"でtypeのspam/No spamの確率を予測
vali_datYes$P <- predict(train.glm2,newdata=vali_datYes,type="response")
#ヒストグラムを描く
par(mfrow=c(1,1),ps=20)
head(vali_datYes$P) #データの形の確認
hist(vali_datYes$P, col = "#ff00ff40", border = "#ff00ff", breaks = 10, xlab="spamの確率", ylim=c(0,500), main="Validate dataのspamの確率")
hist(vali_datNo$P, col = "#0000ff40", border = "#0000ff", breaks = 10, add = TRUE, ylim=c(0,500))
legend("topright",legend=c("Spam","Nonspam"),fill=c("#ff00ff40","#0000ff40")) # #ff00ff40,#0000ff40は半透明色
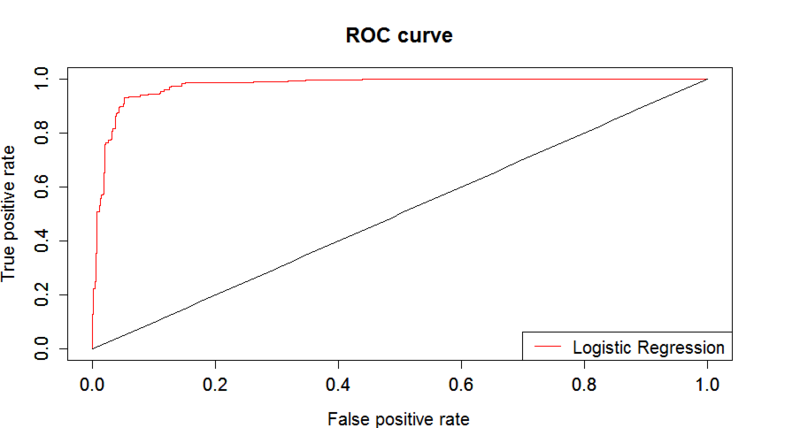
#(d)ROC
#Vali_datの予測結果を踏まえ、ROC curveを描く
par(mfrow=c(1,1)) #グラフレイアウト調整
predicted.p <- predict(train.glm2,newdata=vali_dat2,type="response")
predObj <- prediction(predicted.p,vali_dat2$type)
rocObj <- performance(predObj,measure="tpr",x.measure="fpr")
aucObj <- performance(predObj,measure="auc")
auc <- aucObj@y.values[[1]]
auc
plot(rocObj,main ="ROC curve", col="red")
par(new=T)
y <- function(x) x
plot(y,0,1,xlab="",ylab="")
legend("bottomright",legend=c("Decision Tree"),col=c("red"),lty=c(1))
#(e)R-squared
R2 <- 1-with(train.glm2,deviance/null.deviance)
R2



